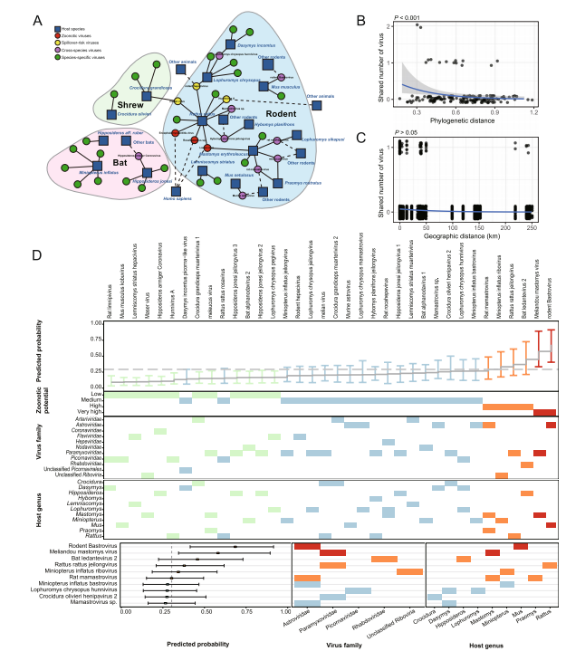
En nylig undersøgelse offentliggjort iMikrobiomudførte viral metagenomisk analyse på 846 vilde små pattedyr - inklusive flagermus, gnavere og spidsmus - indsamlet i Sierra Leone, Vestafrika. Undersøgelsen identificerede i alt 39 pattedyrassocierede RNA-vira, omfattende 26 nye og 13 tidligere kendte vira. Blandt disse udviste Paramyxoviridae-familien den højeste diversitet, mens gnavere indeholdt det største antal virale arter (n = 26).
En zoonotisk risikovurdering afslørede tre kendte zoonotiske vira - encephalomyocarditis-virus, Lassa-virus og Rocahepevirus sp. - samt tre vira med potentiel spillover-risiko: Melian-virus, gnaverhepatitis-virus og Hunnivirus A. Blandt de nyligt identificerede vira viste Bat ledantevirus 2 det tætteste fylogenetiske slægtskab med den menneskeinficerende Le Dantec-virus. Serologisk analyse påviste yderligere neutraliserende antistoffer mod denne virus hos 2,8 % af de lokale beboere, hvilket tyder på tidligere, sandsynligvis uopdaget, menneskelig eksponering.
Disse resultater fremhæver tilstedeværelsen af et betydeligt gnaverdomineret virusreservoir i Vestafrika og understreger den kritiske betydning af integrerede overvågningsstrategier i grænsefladen mellem mennesker og dyr. Kombinationen af metagenomisk screening og serologisk validering giver en robust ramme for identifikation af vira med zoonotisk og spillover-potentiale.

I løbet af det seneste årti er mere end 60 % af nye infektionssygdomme hos mennesker opstået i dyrereservoirer, hvor flagermus, gnavere og spidsmus er anerkendt som vigtige værter for zoonotiske vira. Afrika betragtes bredt som et hotspot for zoonotiske sygdomme. For eksempel rapporterede Sierra Leone over 28.000 tilfælde under ebolaudbruddet i 2014-2016.
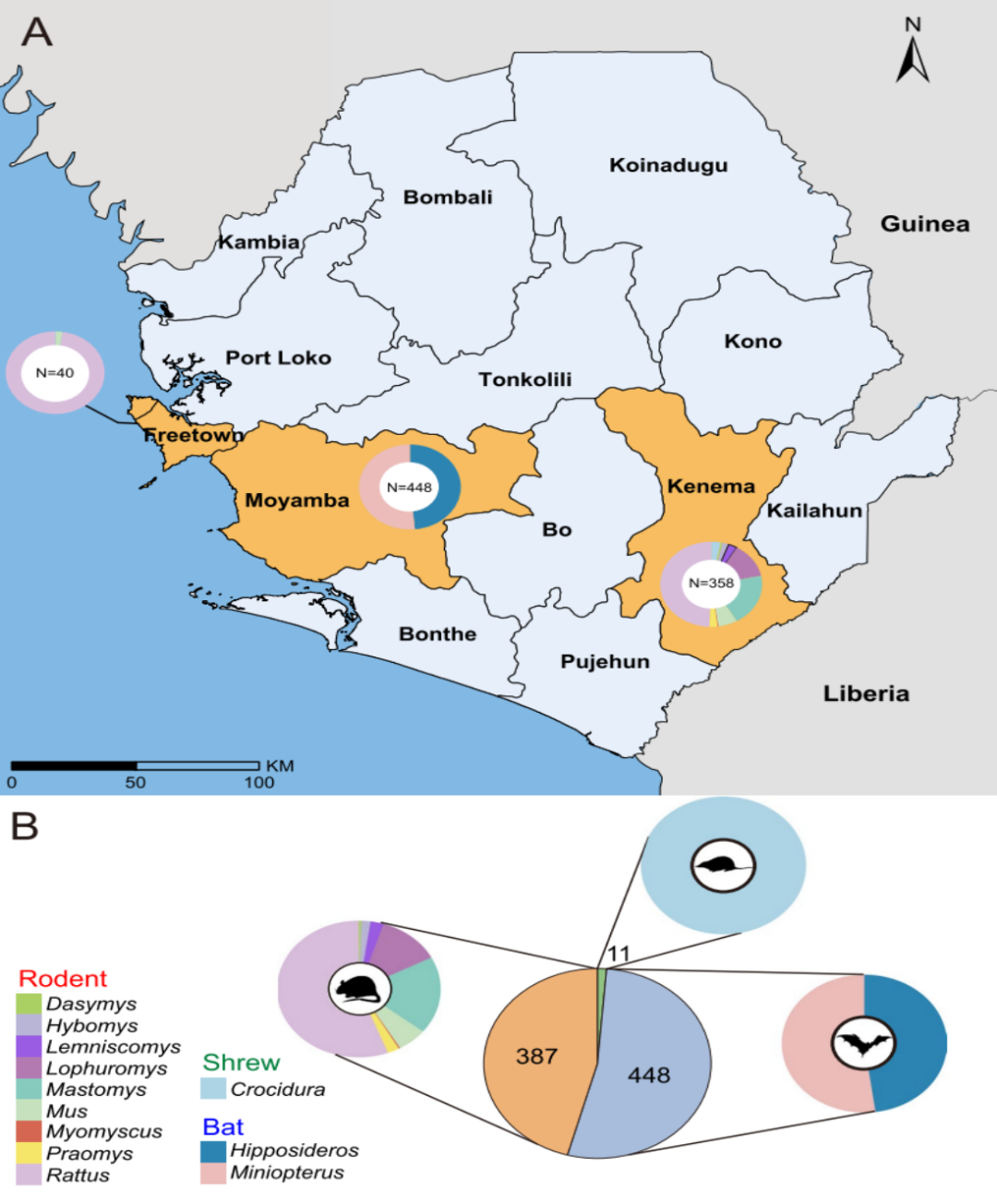
Trods den betydelige byrde af zoonotiske sygdomme i denne region er diversiteten og fordelingen af virus hos vilde små pattedyr fortsat utilstrækkeligt karakteriseret. For at afhjælpe dette hul udførte forskere en systematisk viromanalyse af 846 vilde små pattedyr fanget på tværs af tre steder i Sierra Leone mellem 2018 og 2023. Undersøgelsen havde til formål at karakterisere viral diversitet, identificere kandidater med potentiale for tværartssmitte, vurdere zoonotisk risiko og generere evidens til støtte for tidlige varslingssystemer for nye infektionssygdomme.
Kernemetoder
Undersøgelsen anvendte en omfattende viral metagenomisk arbejdsgang:
- Prøvebehandling:Hjerte-, lever-, milt-, lunge- og nyrevæv blev indsamlet, samlet, homogeniseret og underkastet total RNA-ekstraktion.
- Sekventering og samling:Ribosomalt RNA-depletion blev udført før bibliotekskonstruktion, efterfulgt af højkapacitetssekventering ved hjælp af Illumina NovaSeq 6000-platformen. Virale contigs blev samlet de novo.
- Virusidentifikation:Virus blev identificeret baseret på RNA-afhængig RNA-polymerase (RdRp) genjustering. Kun vira associeret med hvirveldyr blev bevaret, eksklusive bakterie-, svampe- og plantevirus.
- Bioinformatisk analyse:Der blev udført fylogenetisk rekonstruktion, rekombinationsanalyse, modellering af transmissionsnetværk på tværs af arter og zoonotisk risikovurdering.
- Serologisk validering:Et VSV-baseret pseudovirus-neutraliseringsassay blev udviklet til Bat ledantevirus 2. Neutraliserende antistoffer blev påvist i 2,8% af humane sera, hvilket giver tegn på potentiel zoonotisk transmission.
StudereResultater
1. Viral opdagelse og diversitet
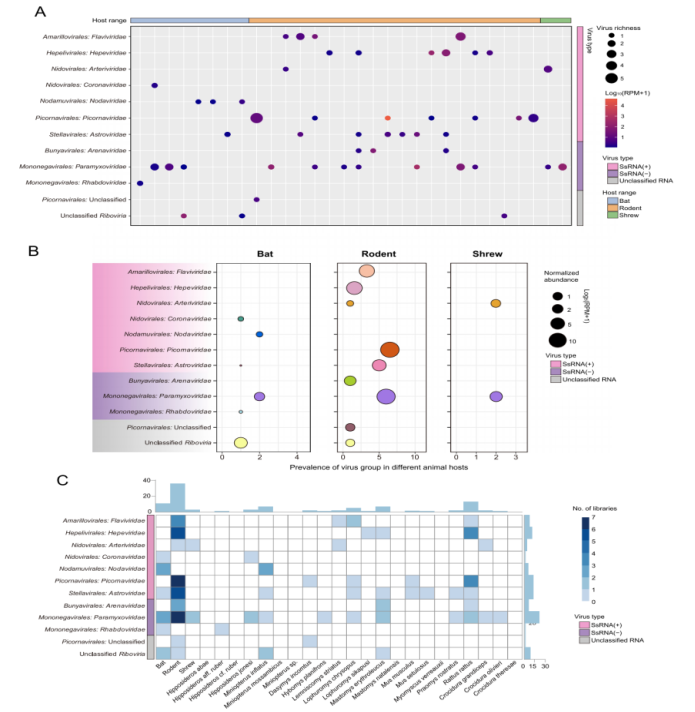
Dette studie udførte transkriptomisk sekventeringsanalyse på 846 vilde dyr indsamlet i Sierra Leone, herunder gnavere, flagermus og spidsmus. Baseret på komplette RNA-afhængige RNA-polymerase (RdRp) gensekvenser blev i alt 39 pattedyrassocierede RNA-vira identificeret, omfattende 13 tidligere kendte vira og 26 nye vira.
Med hensyn til virussammensætning udviste Paramyxoviridae-familien det højeste niveau af diversitet på tværs af alle tre værtsordener, efterfulgt af Astroviridae og Picornaviridae. Med hensyn til værtsfordeling bidrog gnavere med den største virale diversitet og husede i alt 26 virusarter, hvilket indikerer deres fremtrædende rolle som reservoirer for viral diversitet i regionen.
2. Zoonotisk risiko
En zoonotisk risikovurdering identificerede tre kendte zoonotiske vira: encephalomyocarditis-virus, Lassa-virus og Rocahepevirus-arter. Derudover blev tre vira - Melian-virus, gnaverhepatitisvirus og Hunnivirus A - identificeret som havende potentiel risiko for afsmittelse.
Blandt de 26 nyopdagede vira blev fire forudsagt at have et højt zoonotisk potentiale baseret på fylogenetiske og genomiske karakteristika. Især Bat ledantevirus 2 viste det tætteste fylogenetiske slægtskab med den kendte menneskeinficerende Le Dantec-virus.
Efterfølgende serologisk undersøgelse understøttede yderligere dette fund, da neutraliserende antistoffer mod Bat ledantevirus 2 blev påvist i 2,8% af sera fra lokale beboere. Dette resultat tyder på, at uopdagede eller asymptomatiske infektioner allerede kan være forekommet i den menneskelige befolkning, hvilket fremhæver en potentiel, men tidligere uopdaget zoonotisk smittevej.
3. Dynamik i transmission på tværs af arter
Analyse af artsoverførsel viste, at gnavere indtager en central position i det virale delingsnetværk, hvor de fungerer som nøgleknuder, der letter virusudveksling mellem værtsarter. I alt 15 vira blev identificeret som havende potentiale for artsoverførsel.
Yderligere analyse af transmissionsmønstre på tværs af ordener indikerede, at virusdeling forekom hyppigere mellem værter inden for samme taksonomiske orden, hvilket tyder på, at værtsrelaterethed spiller en vigtig rolle i transmissionsdynamikken. I modsætning hertil udviste flagermus en relativt lavere kapacitet til transmission på tværs af ordener.
Det er vigtigt at bemærke, at der blev observeret tegn på udvidelse af værtsrækkevidden hos visse vira. For eksempel blev Melian-virus, som tidligere blev betragtet som specifik for spidsmus, også påvist hos gnavere i dette studie, hvilket indikerer et potentielt skift i værtens tilpasningsevne og en øget risiko for bredere transmission.
Konklusioner og folkesundhedsmæssige konsekvenser
- Høj viromdiversitet hos vilde små pattedyr:Opdagelsen af 39 RNA-vira, herunder 26 nye arter, afslører et stort virusreservoir i regionen og rapporterer for første gang nye vira med højt zoonotisk potentiale (f.eks. Bat ledantevirus 2).
- Gnavere som prioriterede overvågningsmål:Gnavere fungerer som centrale knudepunkter for virusoverførsel og bærer den højeste virale diversitet, hvilket repræsenterer den største risiko for afsmittelse.
- Behov for integrerede overvågningsstrategier:Resultaterne understøtter prioriteringen af gnavere i aktive overvågningsprogrammer og implementeringen af integrerede tilgange, der kombinerer metagenomik, serologi og økologisk overvågning i grænsefladerne mellem mennesker og dyreliv.
Samlet set leverer denne undersøgelse afgørende beviser til støtte for tidlige varslingssystemer og risikovurderingsrammer for nye zoonotiske sygdomme, hvilket understreger vigtigheden af proaktiv overvågning i højrisikoregioner.
Produktinformation
Opslagstidspunkt: 23. marts 2026